1A.data - DataFrame et Matrice#
Links: notebook, html, python, slides, GitHub
Les DataFrame se sont imposés pour manipuler les données avec le module pandas. Le module va de la manipulation des données jusqu’au calcul d’une régresion linéaire.
Avec cette façon de représenter les données, associée à des un ensemble de méthodes couramment utilisées, ce qu’on faisait en une ou deux boucles se fait maintenant en une seule fonction. Cette séance contient beaucoup d’exemples et peu d’exercices. Il est conseillé de supprimer toutes les sorties et de les exécuter une à une.
from jyquickhelper import add_notebook_menu
add_notebook_menu()
L’introduction ne contient pas d’éléments nécessaires à la réalisation du TD.
Trouver chaussure à ses stats#
La programmation est omni-présente lorsqu’on manipule des données. On leur applique des traitements parfois standards, souvent adaptés pour la circonstance. On souhaite toujours programmer le moins possible mais aussi ne pas avoir à réapprendre un langage à chaque fois qu’on doit manipuler les données.
Le logiciel MATLAB a proposé voici 30 ans un premier environnement de travail facilitant le calcul matriciel et ce standard s’est imposé depuis. Comme MATLAB est un logiciel payant, des équivalents open source et gratuits ont été développés. Ils proposent tous le calcul matriciel, la possibilité de visualiser, un environnement de développement. Ils différent pas des performances différentes et des éventails d’extensions différentes.
R : la référence pour les statisticiens, il est utilisé par tous les chercheurs dans ce domaine.
Octave : clone open source de MATLAB, il n’inclut pas autant de librairies mais il est gratuit.
Julia : c’est le plus jeune, il est plus rapide mais ses librairies sont moins nombreuses.
Ils sont tous performants en qui concerne le calcul numérique, ils le sont beaucoup moins lorsqu’il s’agit de faire des traitements qui ne sont pas numériques (traiter du texte par exemple) car ils n’ont pas été prévus pour cela à la base (à l’exception de Julia peut être qui est plus jeune Python v. Clojure v. Julia). Le langage Python est devenu depuis 2012 une alternative intéressante pour ces raisons (voir également Why Python?) :
Il propose les même fonctionnalités de base (calcul matriciel, graphiques, environnement).
Python est plus pratique pour tout ce qui n’est pas numérique (fichiers, web, server web, SQL, …).
La plupart des librairies connues et écrites en C++ ont été portée sous Python.
Il est plus facile de changer un composant important en Python (numpy par exemple) si le nouveau est plus efficace.
Un inconvénient peut-être est qu’il faut installer plusieurs extensions avant de pouvoir commencer à travailler (voir Installation de Python) :
numpy : calcul matriciel
pandas : DataFrame
jupyter : notebooks (comme celui-ci)
matplotlib : graphiques
scikit-learn : machine learning, statistique descriptive
statsmodels : statistiques descriptives
Optionnels :
Spyder : environnement type R, MATLAB, …
scipy : autres traitements numériques (voir NumPy vs. SciPy vs. other packages)
dask : dataframe distribué et capables de gérer des gros volumes de données (> 5Go)
Les environnements Python évoluent très vite, les modules mentionnés ici sont tous maintenus mais il eut en surgir de nouveau très rapidement. Quelques environnements à suivre :
Python Tools for Visual Studio : environnement de développement pour Visual Studio
PyCharm : n’inclut pas les graphiques mais est assez agréable pour programmer
IEP : écrit en Python
Si vous ne voulez pas programmer, il existe des alternatives. C’est assez performant sur de petits jeux de données mais cela devient plus complexe dès qu’on veut programmer car le code doit tenir compte des spécificités de l’outil.
Orange : écrit en Python
Weka : écrit en Java (le pionnier)
dataiku : startup française
RapidMiner : version gratuite et payante
AzureML : solution Microsoft de workflow de données
C’est parfois plus pratique pour commencer mais mal commode si on veut automatiser un traitrment pour répéter la même tâche de façon régulière. Pour les travaux pratiques à l’ENSAE, j’ai choisi les notebooks : c’est une page blanche où on peut mélanger texte, équations, graphiques, code et exécution de code.
Taille de DataFrame
Les DataFrame en Python sont assez rapides lorsqu’il y a moins de 10 millions d’observations et que le fichier texte qui décrit les données n’est pas plus gros que 10 Mo. Au delà, il faut soit être patient, soit être astucieux comme ici : DataFrame et SQL, Data Wrangling with Pandas.
Valeurs manquantes
Lorsqu’on récupère des données, il peut arriver qu’une valeur soit manquante.
DataFrame (pandas)#
Quelques liens : An Introduction to Pandas
Un Data Frame est un objet qui est présent dans la plupart des logiciels de traitements de données, c’est une matrice, chaque colonne est de même type (nombre, dates, texte), elle peut contenir des valeurs manquantes. On peut considérer chaque colonne comme les variables d’une table (pandas.Dataframe - cette page contient toutes les méthodes de la classe).
import pandas
l = [ { "date":"2014-06-22", "prix":220.0, "devise":"euros" },
{ "date":"2014-06-23", "prix":221.0, "devise":"euros" },]
df = pandas.DataFrame(l)
df
| date | devise | prix | |
|---|---|---|---|
| 0 | 2014-06-22 | euros | 220 |
| 1 | 2014-06-23 | euros | 221 |
2 rows × 3 columns
Avec une valeur manquante :
l = [ { "date":"2014-06-22", "prix":220.0, "devise":"euros" },
{ "date":"2014-06-23", "devise":"euros" },]
df = pandas.DataFrame(l)
df
| date | devise | prix | |
|---|---|---|---|
| 0 | 2014-06-22 | euros | 220 |
| 1 | 2014-06-23 | euros | NaN |
2 rows × 3 columns
NaN
est une convention pour une valeur manquante. On extrait la variable
prix :
df.prix
0 220
1 NaN
Name: prix, dtype: float64
Ou :
df["prix"]
0 220
1 NaN
Name: prix, dtype: float64
Pour extraire plusieurs colonnes :
df [["date","prix"]]
| date | prix | |
|---|---|---|
| 0 | 2014-06-22 | 220 |
| 1 | 2014-06-23 | NaN |
2 rows × 2 columns
Pour prendre la transposée (voir aussi DataFrame.transpose) :
df.T
| 0 | 1 | |
|---|---|---|
| date | 2014-06-22 | 2014-06-23 |
| devise | euros | euros |
| prix | 220 | NaN |
3 rows × 2 columns
Lecture et écriture de DataFrame#
Aujourd’hui, on n’a plus besoin de réécrire soi-même une fonction de
lecture ou d’écriture de données présentées sous forme de tables. Il
existe des fonctions plus génériques qui gère un grand nombre de cas.
Cette section présente brièvement les fonctions qui permettent de
lire/écrire un DataFrame aux formats texte/Excel. On reprend l’exemple
de section précédente. L’instruction encoding=utf-8 n’est pas
obligatoire mais conseillée lorsque les données contiennent des accents
(voir
read_csv).
import pandas
l = [ { "date":"2014-06-22", "prix":220.0, "devise":"euros" },
{ "date":"2014-06-23", "prix":221.0, "devise":"euros" },]
df = pandas.DataFrame(l)
# écriture au format texte
df.to_csv("exemple.txt",sep="\t",encoding="utf-8", index=False)
# on regarde ce qui a été enregistré
with open("exemple.txt", "r", encoding="utf-8") as f : text = f.read()
print(text)
# on enregistre au format Excel
df.to_excel("exemple.xlsx", index=False)
# on ouvre Excel sur ce fichier (sous Windows)
from pyquickhelper.loghelper import run_cmd
from pyquickhelper.loghelper.run_cmd import skip_run_cmd
out,err = run_cmd("exemple.xlsx", wait = False)
date devise prix
2014-06-22 euros 220.0
2014-06-23 euros 221.0
On peut récupérer des données directement depuis Internet ou une chaîne de caractères et afficher le début (head) ou la fin (tail). Le code qui suit est ce qu’on écrirait d’habitude :
if False:
import pandas, urllib.request
furl = urllib.request.urlopen("http://www.xavierdupre.fr/enseignement/complements/marathon.txt")
df = pandas.read_csv(furl, sep="\t", names=["ville", "annee", "temps","secondes"])
df.head()
Et pout éviter les erreurs de connexion internet, les données font partie intégrante du module :
from ensae_teaching_cs.data import marathon
import pandas
df = pandas.read_csv(marathon(filename=True),
sep="\t", names=["ville", "annee", "temps","secondes"])
df.head()
| ville | annee | temps | secondes | |
|---|---|---|---|---|
| 0 | PARIS | 2011 | 02:06:29 | 7589 |
| 1 | PARIS | 2010 | 02:06:41 | 7601 |
| 2 | PARIS | 2009 | 02:05:47 | 7547 |
| 3 | PARIS | 2008 | 02:06:40 | 7600 |
| 4 | PARIS | 2007 | 02:07:17 | 7637 |
La fonction describe permet d’en savoir un peu plus sur les colonnes numériques de cette table.
df.describe()
| annee | secondes | |
|---|---|---|
| count | 359.000000 | 359.000000 |
| mean | 1989.754875 | 7933.660167 |
| std | 14.028545 | 385.289830 |
| min | 1947.000000 | 7382.000000 |
| 25% | 1981.000000 | 7698.000000 |
| 50% | 1991.000000 | 7820.000000 |
| 75% | 2001.000000 | 8046.500000 |
| max | 2011.000000 | 10028.000000 |
8 rows × 2 columns
DataFrame et Index#
On désigne généralement une colonne ou variable par son nom. Les lignes peuvent être désignées par un entier.
import pandas
l = [ { "date":"2014-06-22", "prix":220.0, "devise":"euros" },
{ "date":"2014-06-23", "prix":221.0, "devise":"euros" },]
df = pandas.DataFrame(l)
df
| date | devise | prix | |
|---|---|---|---|
| 0 | 2014-06-22 | euros | 220 |
| 1 | 2014-06-23 | euros | 221 |
2 rows × 3 columns
On extrait une ligne (loc) :
df.iloc[1]
date 2014-06-23
devise euros
prix 221
Name: 1, dtype: object
Mais il est possible d’utiliser une colonne ou plusieurs colonnes comme index (set_index) :
dfi = df.set_index("date")
dfi
| devise | prix | |
|---|---|---|
| date | ||
| 2014-06-22 | euros | 220 |
| 2014-06-23 | euros | 221 |
2 rows × 2 columns
On peut maintenant désigner une ligne par une date :
dfi.loc["2014-06-23"]
devise euros
prix 221
Name: 2014-06-23, dtype: object
Il est possible d’utiliser plusieurs colonnes comme index :
df = pandas.DataFrame([ {"prénom":"xavier", "nom":"dupré", "arrondissement":18},
{"prénom":"clémence", "nom":"dupré", "arrondissement":15 } ])
dfi = df.set_index(["nom","prénom"])
dfi.loc["dupré","xavier"]
arrondissement 18
Name: (dupré, xavier), dtype: int64
Si on veut changer l’index ou le supprimer (reset_index) :
dfi.reset_index(drop=False, inplace=True)
# le mot-clé drop pour garder ou non les colonnes servant d'index
# inplace signifie qu'on modifie l'instance et non qu'une copie est modifiée
# donc on peut aussi écrire dfi2 = dfi.reset_index(drop=False)
dfi.set_index(["nom", "arrondissement"],inplace=True)
dfi
| prénom | ||
|---|---|---|
| nom | arrondissement | |
| dupré | 18 | xavier |
| 15 | clémence |
2 rows × 1 columns
Les index sont particulièrement utiles lorsqu’il s’agit de fusionner deux tables. Pour des petites tables, la plupart du temps, il est plus facile de s’en passer.
Notation avec le symbole :#
Le symbole : désigne une plage de valeurs.
from ensae_teaching_cs.data import marathon
import pandas
df = pandas.read_csv(marathon(filename=True),
sep="\t", names=["ville", "annee", "temps","secondes"])
df.head()
| ville | annee | temps | secondes | |
|---|---|---|---|---|
| 0 | PARIS | 2011 | 02:06:29 | 7589 |
| 1 | PARIS | 2010 | 02:06:41 | 7601 |
| 2 | PARIS | 2009 | 02:05:47 | 7547 |
| 3 | PARIS | 2008 | 02:06:40 | 7600 |
| 4 | PARIS | 2007 | 02:07:17 | 7637 |
On peut sélectionner un sous-ensemble de lignes :
df[3:6]
| ville | annee | temps | secondes | |
|---|---|---|---|---|
| 3 | PARIS | 2008 | 02:06:40 | 7600 |
| 4 | PARIS | 2007 | 02:07:17 | 7637 |
| 5 | PARIS | 2006 | 02:08:03 | 7683 |
3 rows × 4 columns
On extrait la même plage mais avec deux colonnes seulement :
df.loc[3:6,["annee","temps"]]
| annee | temps | |
|---|---|---|
| 3 | 2008 | 02:06:40 |
| 4 | 2007 | 02:07:17 |
| 5 | 2006 | 02:08:03 |
| 6 | 2005 | 02:08:02 |
4 rows × 2 columns
Le même code pour lequel on renomme les colonnes extraites :
sub = df.loc[3:6,["annee","temps"]]
sub.columns = ["year","time"]
sub
| year | time | |
|---|---|---|
| 3 | 2008 | 02:06:40 |
| 4 | 2007 | 02:07:17 |
| 5 | 2006 | 02:08:03 |
| 6 | 2005 | 02:08:02 |
4 rows × 2 columns
Exercice 1 : créer un fichier Excel#
On souhaite récupérer les données donnees_enquete_2003_television.txt (source : INSEE).
POIDSLOG: Pondération individuelle relativePOIDSF: Variable de pondération individuellecLT1FREQ: Nombre d’heures en moyenne passées à regarder la télévisioncLT2FREQ: Unité de temps utilisée pour compter le nombre d’heures passées à regarder la télévision, cette unité est représentée par les quatre valeurs suivantes0 : non concerné
1 : jour
2 : semaine
3 : mois
Ensuite, on veut :
Supprimer les colonnes vides
Obtenir les valeurs distinctes pour la colonne
cLT2FREQModifier la matrice pour enlever les lignes pour lesquelles l’unité de temps (cLT2FREQ) n’est pas renseignée ou égale à zéro.
Sauver le résultat au format Excel.
Vous aurez peut-être besoin des fonctions suivantes :
import pandas, io
# ...
Manipuler un DataFrame : filtrer, union, sort, group by, join, pivot#
Si la structure DataFrame s’est imposée, c’est parce qu’on effectue toujours les mêmes opérations. Chaque fonction cache une boucle ou deux dont le coût est précisé en fin de ligne :
filter : on sélectionne un sous-ensemble de lignes qui vérifie une condition
union : concaténation de deux jeux de données
sort : tri
group by : grouper des lignes qui partagent une valeur commune
join : fusionner deux jeux de données en associant les lignes qui partagent une valeur commune
pivot : utiliser des valeurs présentes dans colonne comme noms de colonnes
Les 5 premières opérations sont issues de la logique de manipulation des données avec le langage SQL (ou le logiciel SAS). La dernière correspond à un tableau croisé dynamique. Pour illustrer ces opérations, on prendre le DataFrame suivant :
from ensae_teaching_cs.data import marathon
import pandas
df = pandas.read_csv(marathon(), sep="\t", names=["ville", "annee", "temps","secondes"])
print(df.columns)
print("villes",set(df.ville))
print("annee",list(set(df.annee))[:10],"...")
Index(['ville', 'annee', 'temps', 'secondes'], dtype='object')
villes {'FUKUOKA', 'STOCKOLM', 'PARIS', 'CHICAGO', 'AMSTERDAM', 'BOSTON', 'BERLIN', 'LONDON', 'NEW YORK'}
annee [1947, 1948, 1949, 1950, 1951, 1952, 1953, 1954, 1955, 1956] ...
filter#
Filter consiste à sélectionner un sous-ensemble de lignes du dataframe. Pour filter sur plusieurs conditions, il faut utiliser les opérateurs logique & (et), | (ou), ~ (non) (voir Mapping Operators to Functions).
subset = df [ df.annee == 1971 ]
subset.head()
| ville | annee | temps | secondes | |
|---|---|---|---|---|
| 112 | FUKUOKA | 1971 | 02:12:51 | 7971 |
| 204 | NEW YORK | 1971 | 02:22:54 | 8574 |
| 285 | BOSTON | 1971 | 02:18:45 | 8325 |
subset = df [ (df.annee == 1971) & (df.ville == "BOSTON") ]
subset.head()
| ville | annee | temps | secondes | |
|---|---|---|---|---|
| 285 | BOSTON | 1971 | 02:18:45 | 8325 |
union#
union = concaténation de deux DataFrame (qui n’ont pas nécessaire les mêmes colonnes). On peut concaténer les lignes ou les colonnes.
concat_ligne = pandas.concat((df,df))
df.shape,concat_ligne.shape
((360, 4), (720, 4))
concat_col = pandas.concat((df,df), axis=1)
df.shape,concat_col.shape
((360, 4), (360, 8))
sort#
Sort = trier
tri = df.sort_values( ["annee", "ville"], ascending=[0,1])
tri.head()
| ville | annee | temps | secondes | |
|---|---|---|---|---|
| 35 | BERLIN | 2011 | 02:03:38 | 7418 |
| 326 | BOSTON | 2011 | 02:03:02 | 7382 |
| 203 | LONDON | 2011 | 02:04:40 | 7480 |
| 0 | PARIS | 2011 | 02:06:29 | 7589 |
| 277 | STOCKOLM | 2011 | 02:14:07 | 8047 |
5 rows × 4 columns
group by#
Cette opération consiste à grouper les lignes qui partagent une caractéristique commune (une ou ou plusieurs valeurs par exemple). Sur chaque groupe, on peut calculer une somme, une moyenne…
gr = df.groupby("annee")
gr
<pandas.core.groupby.DataFrameGroupBy object at 0x04887DB0>
nb = gr.count()
nb.sort_index(ascending=False).head()
| ville | annee | temps | secondes | |
|---|---|---|---|---|
| annee | ||||
| 2011 | 5 | 5 | 5 | 5 |
| 2010 | 9 | 9 | 9 | 9 |
| 2009 | 9 | 9 | 9 | 9 |
| 2008 | 9 | 9 | 9 | 9 |
| 2007 | 9 | 9 | 9 | 9 |
5 rows × 4 columns
nb = gr.sum()
nb.sort_index(ascending=False).head(n=2)
| secondes | |
|---|---|
| annee | |
| 2011 | 37916 |
| 2010 | 68673 |
2 rows × 1 columns
nb = gr.mean()
nb.sort_index(ascending=False).head(n=3)
| secondes | |
|---|---|
| annee | |
| 2011 | 7583.200000 |
| 2010 | 7630.333333 |
| 2009 | 7652.555556 |
3 rows × 1 columns
Si les nom des colonnes utilisées lors de l’opération ne sont pas mentionnés, implicitement, c’est l’index qui sera choisi. On peut aussi aggréger les informations avec une fonction personnalisée.
def max_entier(x):
return int(max(x))
nb = df[["annee","secondes"]].groupby("annee").agg(max_entier).reset_index()
nb.tail(n=3)
| annee | secondes | |
|---|---|---|
| 62 | 2009 | 8134 |
| 63 | 2010 | 7968 |
| 64 | 2011 | 8047 |
3 rows × 2 columns
Ou encore considérer des aggrégations différentes pour chaque colonne :
nb = df[["annee","ville","secondes"]].groupby("annee").agg({ "ville":len, "secondes":max_entier})
nb.tail(n=3)
| secondes | ville | |
|---|---|---|
| annee | ||
| 2009 | 8134 | 9 |
| 2010 | 7968 | 9 |
| 2011 | 8047 | 5 |
3 rows × 2 columns
join (merge ou fusion)#
Fusionner deux tables consiste à apparier les lignes de la première table avec celle de la seconde si certaines colonnes de ces lignes partagent les mêmes valeurs. On distingue quatre cas :
INNER JOIN- inner : on garde tous les appariements réussisLEFT OUTER JOIN- left : on garde tous les appariements réussis et les lignes non appariées de la table de gaucheRIGHT OUTER JOIN- right : on garde tous les appariements réussis et les lignes non appariées de la table de droiteFULL OUTER JOIN- outer : on garde tous les appariements réussis et les lignes non appariées des deux tables
Exemples et documentation : * merging, joining * join * merge ou DataFrame.merge * jointures SQL - illustrations avec graphiques en patates
Si les noms des colonnes utilisées lors de la fusion ne sont pas mentionnés, implicitement, c’est l’index qui sera choisi. Pour les grandes tables (> 100.000 lignes), il est fortement recommandés d’ajouter un index s’il n’existe pas avant de fusionner.
A quoi correspondent les quatre cas suivants :
from IPython.display import Image
Image("patates.png")
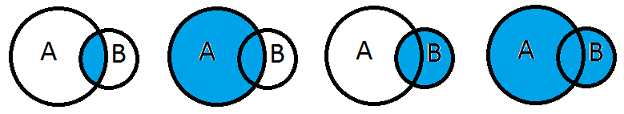
On souhaite ajouter une colonne pays aux marathons se déroulant dans les villes suivanes.
values = [ {"V":'BOSTON', "C":"USA"},
{"V":'NEW YORK', "C":"USA"},
{"V":'BERLIN', "C":"Germany"},
{"V":'LONDON', "C":"UK"},
{"V":'PARIS', "C":"France"}]
pays = pandas.DataFrame(values)
pays
| C | V | |
|---|---|---|
| 0 | USA | BOSTON |
| 1 | USA | NEW YORK |
| 2 | Germany | BERLIN |
| 3 | UK | LONDON |
| 4 | France | PARIS |
5 rows × 2 columns
dfavecpays = df.merge(pays, left_on="ville", right_on="V")
pandas.concat([dfavecpays.head(n=2),dfavecpays.tail(n=2)])
| ville | annee | temps | secondes | C | V | |
|---|---|---|---|---|---|---|
| 0 | PARIS | 2011 | 02:06:29 | 7589 | France | PARIS |
| 1 | PARIS | 2010 | 02:06:41 | 7601 | France | PARIS |
| 193 | BOSTON | 2010 | 02:05:52 | 7552 | USA | BOSTON |
| 194 | BOSTON | 2011 | 02:03:02 | 7382 | USA | BOSTON |
4 rows × 6 columns
pivot (tableau croisé dynamique)#
Cette opération consiste à créer une seconde table en utilisant utiliser les valeurs d’une colonne comme nom de colonnes.
A |
B |
C |
|---|---|---|
A1 |
B1 |
C1 |
A1 |
B2 |
C2 |
A2 |
B1 |
C3 |
A2 |
B2 |
C4 |
A2 |
B3 |
C5 |
L’opération pivot(A,B,C) donnera :
A |
B1 |
B2 |
B3 |
|---|---|---|---|
A1 |
C1 |
C2 |
|
A2 |
C3 |
C4 |
C5 |
On applique cela aux marathons où on veut avoir les villes comme noms de colonnes et une année par lignes.
piv = df.pivot("annee","ville","temps")
pandas.concat([piv[20:23],piv[40:43],piv.tail(n=3)])
| ville | AMSTERDAM | BERLIN | BOSTON | CHICAGO | FUKUOKA | LONDON | NEW YORK | PARIS | STOCKOLM |
|---|---|---|---|---|---|---|---|---|---|
| annee | |||||||||
| 1967 | NaN | NaN | 02:15:45 | NaN | 02:09:37 | NaN | NaN | NaN | NaN |
| 1968 | NaN | NaN | 02:22:17 | NaN | 02:10:48 | NaN | NaN | NaN | NaN |
| 1969 | NaN | NaN | 02:13:49 | NaN | 02:11:13 | NaN | NaN | NaN | NaN |
| 1987 | 02:12:40 | 02:11:11 | 02:11:50 | NaN | 02:08:18 | 02:09:50 | 02:11:01 | 02:11:09 | 02:13:52 |
| 1988 | 02:12:38 | 02:11:45 | 02:08:43 | 02:08:57 | 02:11:04 | 02:10:20 | 02:08:20 | 02:13:53 | 02:14:26 |
| 1989 | 02:13:52 | 02:10:11 | 02:09:06 | 02:11:25 | 02:12:54 | 02:09:03 | 02:08:01 | 02:13:03 | 02:13:34 |
| 2009 | 02:06:18 | 02:06:08 | 02:08:42 | 02:05:41 | 02:05:18 | 02:05:10 | 02:09:15 | 02:05:47 | 02:15:34 |
| 2010 | 02:05:44 | 02:05:08 | 02:05:52 | 02:06:23 | 02:08:24 | 02:05:19 | 02:08:14 | 02:06:41 | 02:12:48 |
| 2011 | NaN | 02:03:38 | 02:03:02 | NaN | NaN | 02:04:40 | NaN | 02:06:29 | 02:14:07 |
9 rows × 9 columns
Il existe une méthode qui effectue l’opération inverse : Dataframe.stack.
Exercice 2 : moyennes par groupes#
Toujours avec le même jeu de données (marathon.txt), on veut ajouter une ligne à la fin du tableau croisé dynamique contenant la moyenne en secondes des temps des marathons pour chaque ville.
Dates#
Les dates sont souvent compliquées à gérer car on n’utilise pas le mêmes format dans tous les pays. Pour faire simple, je recommande deux options :
Soit convertir les dates/heures au format chaînes de caractères
AAAA-MM-JJ hh:mm:ss:msqui permet de trier les dates par ordre croissant.Soit convertir les dates/heures au format datetime (date) ou timedelta (durée) (voir Quelques notions sur les dates, format de date/heure).
Par exemple, voici le code qui a permis de générer la colonne seconde de la table marathon :
from datetime import datetime, time
from ensae_teaching_cs.data import marathon
import pandas
df = pandas.read_csv(marathon(), sep="\t", names=["ville", "annee", "temps","secondes"])
df = df [["ville", "annee", "temps"]] # on enlève la colonne secondes pour la recréer
df["secondes"] = df.apply( lambda r : (datetime.strptime(r.temps,"%H:%M:%S") - \
datetime(1900,1,1)).total_seconds(), axis=1)
df.head()
| ville | annee | temps | secondes | |
|---|---|---|---|---|
| 0 | PARIS | 2011 | 02:06:29 | 7589.0 |
| 1 | PARIS | 2010 | 02:06:41 | 7601.0 |
| 2 | PARIS | 2009 | 02:05:47 | 7547.0 |
| 3 | PARIS | 2008 | 02:06:40 | 7600.0 |
| 4 | PARIS | 2007 | 02:07:17 | 7637.0 |
Matrix, Array (numpy)#
Le module le plus populaire sous Python est
numpy. Il propose deux containers
Matrix
et
Array
qui facilitent le calcul matriciel. Ce module est écrit en C++, Fortran.
Il sera plus rapide que tout code écrit en Python. De nombreuses modules
Python s’appuient sur numpy : SciPy,
pandas,
scikit-learn,
matplotlib, … Il y a deux différences entre
un DataFrame et un tableau numpy :
Il n’y a pas d’index sur les lignes autre que l’index entier de la ligne.
Tous les types doivent être identiques (tous entier, tous réels, tous str). Il n’y a pas de mélange possible. C’est à cette condition que les calculs sont aussi rapides.
import numpy
print("int","\n",numpy.matrix([[1, 2], [3, 4,]]))
print("float","\n",numpy.matrix([[1, 2], [3, 4.1]]))
print("str","\n",numpy.matrix([[1, 2], [3, '4']]))
int
[[1 2]
[3 4]]
float
[[ 1. 2. ]
[ 3. 4.1]]
str
[['1' '2']
['3' '4']]
Il y a deux types d’objets, array et matrix. Le type matrix
se comporte comme on peut l’attendre d’une matrice. Le type array
est plus générique et autorise plus de deux dimensions. Les opérateurs
qui s’y appliquent ne comportent pas comme ceux d’une matrice, en
particulier la multiplication qui se fait terme à terme pour un tableau.
m1 = numpy.matrix( [[0.0,1.0],[1.0,0.0]])
print("multiplication de matrices\n",m1 * m1)
m2 = numpy.array([[0.0,1.0],[1.0,0.0]])
print("multiplication de tableaux (terme à terme)\n",m2 * m2)
multiplication de matrices
[[ 1. 0.]
[ 0. 1.]]
multiplication de tableaux (terme à terme)
[[ 0. 1.]
[ 1. 0.]]
Un tableau en plusieurs dimensions :
cube = numpy.array( [ [[0.0,1.0],[1.0,0.0]],
[[0.0,1.0],[1.0,0.0]] ] )
print(cube.shape)
cube
(2, 2, 2)
array([[[ 0., 1.],
[ 1., 0.]],
[[ 0., 1.],
[ 1., 0.]]])
Quelques liens pour apprendre à manipuler ces objets :
matrices nulle, identité, aléatoire#
On utilise beaucoup les fonctions suivantes pour créer une matrice ou un tableau particulier.
# la matrice nulle
numpy.zeros( (3,4) )
array([[ 0., 0., 0., 0.],
[ 0., 0., 0., 0.],
[ 0., 0., 0., 0.]])
# la matrice de 1
numpy.ones( (3,4) )
array([[ 1., 1., 1., 1.],
[ 1., 1., 1., 1.],
[ 1., 1., 1., 1.]])
# la matrice identité
numpy.identity( 3 )
array([[ 1., 0., 0.],
[ 0., 1., 0.],
[ 0., 0., 1.]])
# la matrice aléatoire
numpy.random.random( (3,4))
array([[ 0.56295296, 0.77545561, 0.56041393, 0.90371888],
[ 0.09984123, 0.59781939, 0.09845057, 0.30856921],
[ 0.37161512, 0.5630934 , 0.6359542 , 0.13298039]])
Pour d’autres fonctionnalités aléatoires : numpy.random.
Quelques fonctions fréquemment utilisées#
column_stack : pour assembler des colonnes les unes à côté des autres
vstack : pour assembler des lignes les unes à la suite des autres
de DataFrame à numpy#
Le plus simple est sans doute d’utiliser pandas pour lire un fichier
texte et d’utiliser la propriété
values
pour convertir tout ou partie du DataFrame en numpy.matrix.
from pandas import read_csv
import numpy
from datetime import datetime, time
from ensae_teaching_cs.data import marathon
df = read_csv(marathon(filename=True),
sep="\t", names=["ville", "annee", "temps","secondes"])
arr = df[["annee","secondes"]].values # retourne un array (et non un matrix)
mat = numpy.matrix(arr)
print(type(arr),type(mat))
arr[:2,:]
<class 'numpy.ndarray'> <class 'numpy.matrixlib.defmatrix.matrix'>
array([[2011, 7589],
[2010, 7601]], dtype=int64)
La conversion réciproque est aussi simple mais il faut préciser les noms
des colonnes qui ne sont pas mémorisées dans l’objet numpy.array :
import pandas
df2 = pandas.DataFrame(arr, columns=["annee", "secondes"])
df2.head(n=2)
| annee | secondes | |
|---|---|---|
| 0 | 2011 | 7589 |
| 1 | 2010 | 7601 |
2 rows × 2 columns
Exercice 3 : régression linéaire#
On souhaite implémenter une
régression
qui se traduit par le problème suivant : . La
solution est donnée par la formule matricielle :
. On prépare les données suivantes.
from pandas import read_csv
from datetime import datetime, time
from ensae_teaching_cs.data import marathon
df = read_csv(marathon(filename=True),
sep="\t", names=["ville", "annee", "temps","secondes"])
df = df [ (df["ville"] == "BERLIN") | (df["ville"] == "PARIS") ]
for v in ["PARIS","BERLIN"]:
df["est" + v] = df.apply( lambda r : 1 if r["ville"] == v else 0, axis=1)
df.head(n = 3)
| ville | annee | temps | secondes | estPARIS | estBERLIN | |
|---|---|---|---|---|---|---|
| 0 | PARIS | 2011 | 02:06:29 | 7589 | 1 | 0 |
| 1 | PARIS | 2010 | 02:06:41 | 7601 | 1 | 0 |
| 2 | PARIS | 2009 | 02:05:47 | 7547 | 1 | 0 |
On veut construire le modèle :
. En
appliquant la formule ci-dessus, déterminer les coefficients
.
Annexes#
Créer un fichier Excel avec plusieurs feuilles#
La page Allow ExcelWriter() to add sheets to existing workbook donne plusieurs exemples d’écriture.
import pandas
writer = pandas.ExcelWriter('tou_example.xlsx')
df.to_excel(writer, 'Data 0')
df.to_excel(writer, 'Data 1')
writer.save()